Laure-Emmanuelle Zaragosi1, d’après une interview réalisée par Agnès Lara
- Chercheuse Inserm à l’Institut de pharmacologie moléculaire et cellulaire de Sophia Antipolis (Valbonne)
Alors que la France ambitionne de devenir leader dans la recherche en biologie cellulaire, l’Institut de pharmacologie moléculaire et cellulaire (IPMC) de Sophia Antipolis et le service de pneumologie du CHU de Nice travaillent de concert à l’élaboration du premier atlas cellulaire du poumon humain.
Au sein de l’IPMC, le Dr Laure-Emmanuelle Zaragosi coordonne la réalisation de cet atlas. Elle nous en explique les avancées et les retombées potentielles.
Pouvez-vous nous rappeler ce qu’est l’atlas cellulaire du poumon humain et dans quel contexte il a vu le jour ?
> Laure-Emmanuelle Zaragosi : L’atlas cellulaire du poumon humain s’inscrit dans le cadre d’un consortium international, l’atlas cellulaire du corps humain ou Human Cell Atlas (HCA), qui vise à cartographier l’ensemble des cellules humaines. Lancé en 2016, ce projet colossal mobilise pas moins de 3 600 chercheurs à travers le monde, dont une dizaine d’équipes en Europe. Il est souvent comparé au séquençage du génome humain pour son potentiel révolutionnaire en biologie humaine. En France, deux équipes fondatrices de l’Institut Hospitalo- Universitaire (IHU) RespirERA sont impliquées : d’abord celle de Pascal Barbry, chef de l’équipe Physiologie génomique des eucaryotes à l’Institut de Pharmacologie Moléculaire et Cellulaire (IPMC – CNRS UMR 7275, Inserm U1323 et Université Côte d’Azur) ; et parallèlement celle du Pr Charles Hugo Marquette, responsable du service de pneumologie du CHU de Nice & Université Côte d’Azur, et de la Pr Sylvie Leroy, PU-PH dans ce même service, qui sont officiellement affiliés à l’équipe de Pascal Barbry dès le début de ce projet afin de réaliser les biopsies chez les donneurs sains. L’atlas cellulaire du poumon humain constitue ainsi la première description de l’ensemble des cellules de cet organe chez le sujet sain. Il permettra de mieux comprendre le fonctionnement de chacune d’entre elles et leurs interactions. Il fournit d’ores et déjà une base de données de référence pour étudier des tissus pulmonaires pathologiques.
Où en est aujourd’hui la réalisation de cet atlas ?
Laure-Emmanuelle Zaragosi : Réalisé à partir des données transcriptomiques de 486 individus, dont 107 sujets sains, et de 2,2 millions de cellules, l’atlas cellulaire du poumon humain sain est aujourd’hui terminé. Alors que l’on s’attendait à un nombre limité de cellules différentes dans cet organe, les données collectées ont permis d’identifier 61 types cellulaires, notamment des types cellulaires rares inconnus jusque-là et qui jouent un rôle
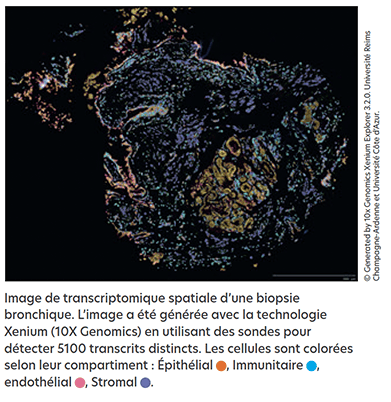
© Generated by 10x Genomics Xenium Explorer 3.2.0. Université Reims Champagne-Ardenne et Université Côte d’Azur.
Image de transcriptomique spatiale d’une biopsie bronchique. L’image a été générée avec la technologie Xenium (10X Genomics) en utilisant des sondes pour détecter 5100 transcrits distincts. Les cellules sont colorées selon leur compartiment : Épithélial , Immunitaire , endothélial , Stromal .
important dans des pathologies comme la mucoviscidose ou le cancer du poumon par exemple. La technique de single cell RNA sequencing (ou scRNA-seq, voir encadré ci-joint) utilisée pour le réaliser permet d’attribuer des gènes marqueurs à chaque type de cellule et de mettre en évidence des modules de gènes spécifiquement associés à des paramètres démographiques ou à des localisations anatomiques au sein du système respiratoire1.[…]
Recherche Atlas cellulaire du poumon humain : un pas de géant vers la médecine de précision
18 _ Info Respiration _ #187 _ Juin 2025 www.splf.fr
Article réservé aux abonné.e.s à Info Respiration u003ca href=u0022https://splf.fr/abonnement-info-respiration/u0022u003eS’abonneru003c/au003en• Si vous êtes abonné.e, connectez-vous u003ca href=u0022https://splf.fr/login/u0022u003ehttps://splf.fr/login/u003c/au003e
- Sikkema L, Strobl D, Zappia L, Madissoon E, Markov N, Zaragosi L, et al. An integrated cell atlas of the human lung in health and disease. Nat Med 2023;1563–77. ↩



